Genie3是目前基因调控网络重建领域最受推崇的AI工具之一,依靠集成学习(如随机森林)算法,能高效挖掘基因间复杂调控关系。本文详细阐释了Genie3的技术原理、使用方法、优势性能及其在疾病研究、单细胞组学、合成生物等高端前沿领域的广泛应用场景。对于从事基因表达数据深度挖掘的科研人员而言,Genie3是不可多得的生信利器。

Genie3详解:基因调控网络重建的强大AI工具及其应用场景解析
Genie3简介与技术原理
什么是Genie3?
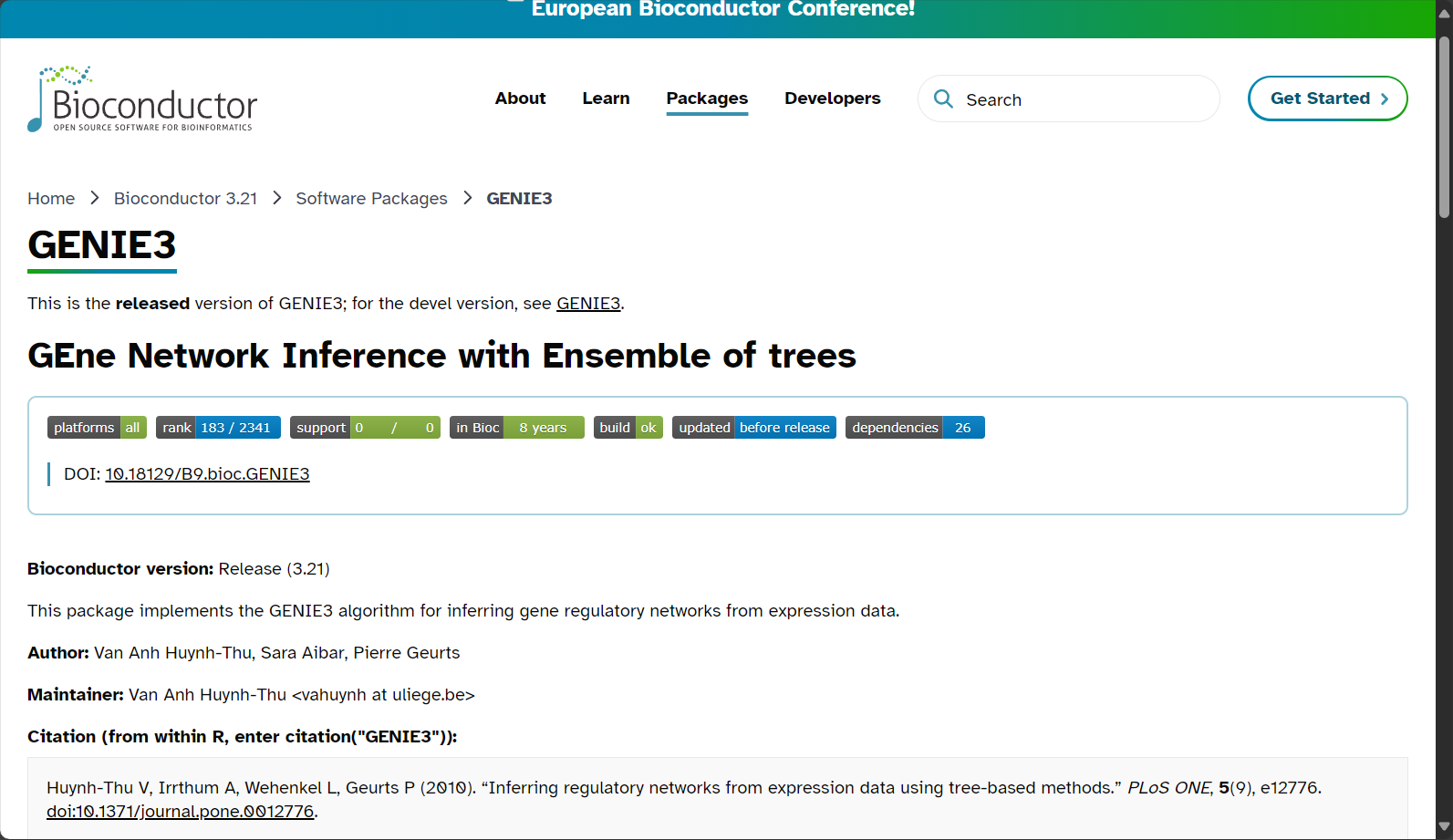
Genie3是一种基于人工智能的基因调控网络(Gene Regulatory Network, GRN)推断工具,由法国INRIA研究所开发,凭借其卓越的特征选择机制与泛化性能,在基因表达数据驱动的网络重建领域中脱颖而出。Genie3能够利用高通量转录组数据,揭示基因之间潜在调控关系,为生命复杂调控机制、疾病分子标志物及合成生物研究等提供了坚实的数据基础。
其优势还在于灵活数据输入、创新AI算法(尤其是随机森林与极端随机树)支持,以及国际知名权威机构(如Nature Methods大型评测)的一致好评。
相关资源:
- 官方网站与指南:Genie3 Bioconductor页面
- 学术原文:Nature Methods论文
Genie3的核心技术——集成学习
Genie3核心源于集成学习算法(随机森林、极端随机树),用于基于基因表达预测的回归模型:
- 为每个基因建立独立多变量回归模型
- 将其他基因(特别是候选调控因子)的表达量作为特征输入,目标基因表达为输出
- 综合各特征的重要性得分,量化调控关系强弱
- 所有预测模型的计算结果整合为加权网络矩阵,反映全部基因调控权重
算法流程简明摘要:
| 步骤 | 描述 |
|---|---|
| 数据导入 | 读取标准化的表达矩阵(行:基因,列:样本) |
| 候选集定义 | 选定转录因子/调控因子列表 |
| 模型训练 | 每个基因独立回归,输入为其它基因表达 |
| 重要性排序 | 统计特征重要性,量化调节点影响 |
| 导出结果 | 输出基因对与权重,后用于网络可视化分析 |
Genie3的优势与性能
- 非参数适应复杂生物数据
- 鲁棒性强,对噪声与冗余抗性好
- 支持多组学样本和单细胞类型分析
- 分析流程自动化,设置简便
- 在DREAM5国际竞赛中评为顶尖算法之一
Genie3的使用方法及数据流程
数据准备及输入格式
Genie3的数据要求:
- 行为基因(Gene),列为样本(Sample)
- 单元格为表达量(如计数、TPM、FPKM、RPKM、log转化值等)
- 适合Bulk RNA-Seq、Microarray、Single-cell RNA-Seq等主流生信数据
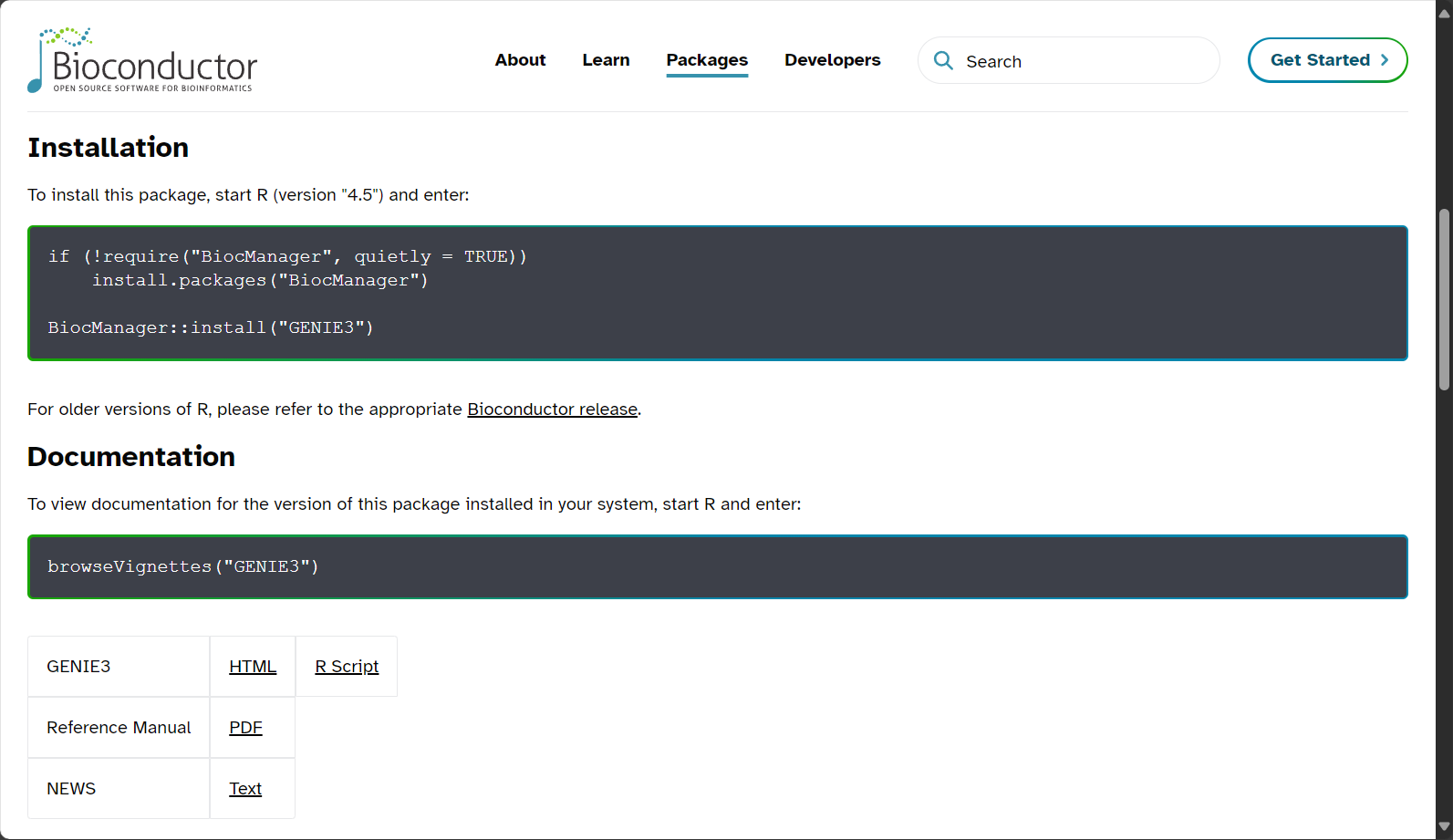
安装与使用方法
Genie3主要于R/Bioconductor安装:
if (!requireNamespace("BiocManager", quietly=TRUE))
install.packages("BiocManager")
BiocManager::install("GENIE3")
基本调用步骤:
library(GENIE3)
# 构造表达矩阵
exprMatr <- matrix(sample(1:10, 100, replace=TRUE), nrow=20)
rownames(exprMatr) <- paste("Gene", 1:20, sep="")
colnames(exprMatr) <- paste("Sample", 1:5, sep="")
# 指定候选调节因子
regulators <- c("Gene2", "Gene4", "Gene7")
# 运行Genie3推断网络
weightMat <- GENIE3(exprMatr, regulators=regulators, treeMethod="ET", K=7, nTrees=50)
# 结果链表获取
linkList <- getLinkList(weightMat)

主要参数汇总:
| 参数 | 说明 | 常见选择 |
|---|---|---|
| exprMatrix | 输入表达矩阵 | 必须 |
| regulators | 候选调控因基因名 | 建议转录因子列表 |
| treeMethod | 树模型类型 | “RF”/“ET” |
| nTrees | 森林树数量 | 50~1000 |
| K | 每次分割特征数 | 默认√N |
结果解读与网络输出
- 输出为加权邻接矩阵,每行对应目标基因、列为调控因子,数值代表调控强度
- 可通过
getLinkList()获得“调节因子-靶基因-权重”三元组,便于后续排序与可视化分析 - 可针对实际需求筛选Top调控关系用于富集挖掘
示例输出:
| 调控因子 | 靶基因 | 权重 |
|---|---|---|
| Gene2 | Gene5 | 0.2111 |
| Gene4 | Gene19 | 0.1902 |
| Gene7 | Gene13 | 0.1709 |

Genie3应用场景解析
疾病生物标志物与复杂疾病发病机制研究
Genie3广泛用于癌症、免疫性疾病、罕见病的调控网络解析,可通过患者与对照样本数据挖掘关键调控因子,绘制病理网络,揭示异常表达背后的调控根源。相关领域如人类基因组网络重建、乳腺癌转录因子筛查等均积极采用Genie3。
单细胞RNA测序与异质性分析
在单细胞转录组(scRNA-seq)盛行的趋势下,Genie3衍生出专为单细胞数据设计的分析框架(如SCENIC),实现细胞状态特异调控模块与亚群异质性分析。
SCENIC流程简表:
| 步骤 | Genie3作用 | 下游分析 |
|---|---|---|
| Co-expression | 探测调控对 | RcisTarget |
| Motif Enrichment | 得分筛选 | AUCell |
| Module Building | 建立亚群网络 | Cytoscape等可视化 |

合成生物与功能基因组工程
在微生物基因工程与合成网络设计领域,Genie3可逆推出自然系统调控逻辑,为人工环路设计和调控模块优化提供岩实的数据支持。常见于大肠杆菌、酵母、植物等模型生物系统。
网络可视化与生信集成
Genie3导出的加权邻接表格可直接导入Cytoscape、Gephi等主流平台,联动转录因子数据库(TRRUST、TRANSFAC)与富集分析,支持端到端的数据挖掘链路。
AI分析集成的前沿应用
Genie3高度兼容主流生信分析平台(scanpy, Seurat, WGCNA),可部署于云计算与高性能计算管道。成为癌症进化、药物反应预测、组学联合数据建模等多领域网络分析重要引擎。
Genie3对比其他网络分析工具
| 工具名称 | 算法原理 | 特点 | 缺点 |
|---|---|---|---|
| Genie3 | 随机森林回归 | 定量调控强度、抗噪优异 | 耗时较长,需高内存 |
| ARACNE | 互信息,降噪剪枝 | 经典,适合大规模筛选 | 二元输出,参数多 |
| WGCNA | 加权相关性网络 | 模块检测好,适合大样本 | 无定向调控,零循因果 |
| CLR | 互信息 z-score | 无监督,算法快 | 调控方向区分弱 |
Genie3因强大的定量调控推断和优异的抗噪能力,成为复杂网络分析的首选AI工具。

结语
Genie3凭借卓越AI建模力、可靠的基因调控推断、灵活契合多场景的能力,已成为分子生物学、转录组、单细胞组学研究的必备利器。
不论是疾病机制解析、合成生物设计,还是生信管道自动化,Genie3都为科研数据深度挖掘建立了坚实基础。目前Genie3迭代快速、社区支持丰富,在生命科学AI工具生态中日益重要。对于欲开展基因调控网络深层研究的科研人员,Genie3是值得信赖的优选平台。
更多详细案例和数据参见官方文档与国际前沿学术论文。
© 版权声明
文章版权归作者所有,未经允许请勿转载。
相关文章

暂无评论...